Instructions to use MIL-UT/Med-Asagi-14B-reasoning_beta with libraries, inference providers, notebooks, and local apps. Follow these links to get started.
- Libraries
- Transformers
How to use MIL-UT/Med-Asagi-14B-reasoning_beta with Transformers:
# Use a pipeline as a high-level helper from transformers import pipeline pipe = pipeline("image-text-to-text", model="MIL-UT/Med-Asagi-14B-reasoning_beta", trust_remote_code=True)# Load model directly from transformers import AutoProcessor, AutoModelForImageTextToText processor = AutoProcessor.from_pretrained("MIL-UT/Med-Asagi-14B-reasoning_beta", trust_remote_code=True) model = AutoModelForImageTextToText.from_pretrained("MIL-UT/Med-Asagi-14B-reasoning_beta", trust_remote_code=True) - Notebooks
- Google Colab
- Kaggle
- Local Apps
- vLLM
How to use MIL-UT/Med-Asagi-14B-reasoning_beta with vLLM:
Install from pip and serve model
# Install vLLM from pip: pip install vllm # Start the vLLM server: vllm serve "MIL-UT/Med-Asagi-14B-reasoning_beta" # Call the server using curl (OpenAI-compatible API): curl -X POST "http://localhost:8000/v1/completions" \ -H "Content-Type: application/json" \ --data '{ "model": "MIL-UT/Med-Asagi-14B-reasoning_beta", "prompt": "Once upon a time,", "max_tokens": 512, "temperature": 0.5 }'Use Docker
docker model run hf.co/MIL-UT/Med-Asagi-14B-reasoning_beta
- SGLang
How to use MIL-UT/Med-Asagi-14B-reasoning_beta with SGLang:
Install from pip and serve model
# Install SGLang from pip: pip install sglang # Start the SGLang server: python3 -m sglang.launch_server \ --model-path "MIL-UT/Med-Asagi-14B-reasoning_beta" \ --host 0.0.0.0 \ --port 30000 # Call the server using curl (OpenAI-compatible API): curl -X POST "http://localhost:30000/v1/completions" \ -H "Content-Type: application/json" \ --data '{ "model": "MIL-UT/Med-Asagi-14B-reasoning_beta", "prompt": "Once upon a time,", "max_tokens": 512, "temperature": 0.5 }'Use Docker images
docker run --gpus all \ --shm-size 32g \ -p 30000:30000 \ -v ~/.cache/huggingface:/root/.cache/huggingface \ --env "HF_TOKEN=<secret>" \ --ipc=host \ lmsysorg/sglang:latest \ python3 -m sglang.launch_server \ --model-path "MIL-UT/Med-Asagi-14B-reasoning_beta" \ --host 0.0.0.0 \ --port 30000 # Call the server using curl (OpenAI-compatible API): curl -X POST "http://localhost:30000/v1/completions" \ -H "Content-Type: application/json" \ --data '{ "model": "MIL-UT/Med-Asagi-14B-reasoning_beta", "prompt": "Once upon a time,", "max_tokens": 512, "temperature": 0.5 }' - Docker Model Runner
How to use MIL-UT/Med-Asagi-14B-reasoning_beta with Docker Model Runner:
docker model run hf.co/MIL-UT/Med-Asagi-14B-reasoning_beta
Model Details
Model Description
Med-Asagi は、日本語の医療画像理解を目的として構築した大規模視覚言語モデル(VLM)です。
医療画像と日本語テキストを統合して扱うことができ、画像に対する質問応答や読影支援のようなタスクに利用できます。
本モデルは、医療分野で利用しやすいオープンな日本語医療 VLMの実現を目的として開発されました。ベースアーキテクチャには LLaVA 系の構成を採用し、画像エンコーダに SigLIP、日本語医療 LLM をテキストデコーダとして組み合わせています。総パラメータ数は約 14B です。
注意
本モデルは開発途中のプロトタイプ(ベータ版)です。現時点では性能が十分でない可能性がある点にご注意ください。
言語処理学会発表
言語処理学会の投稿後にモデルの改変(公開可能モデルに変更・学習方法変更)を行ったため、発表した内容とは異なります。そのため、発表内容が再現しないことがありますことをご了解ください。 変更点は以下の3つです。
- LLMをSIP-med-LLM/SIP-jmed-llm-3-13b-OP-4k-baseに変更
- Image encoderをgoogle/siglip2-so400m-patch16-512に変更
- 学習ステージを3段階に変更(Stage2として、Enriched captionの学習を新たに追加)
モデルの特徴
- 日本語の医療画像タスクに特化した視覚言語モデル
- 約 1,200 万件規模の日本語医療学習データを用いて学習
- 推論過程を明示的に出力する Reasoning / CoT 形式 の学習データで訓練
- CT 画像および胸部 X 線画像の評価で、既存のオープン VLM と比較して高い性能を確認
本研究では、通常の応答のみを生成するモデルに加えて、<description> と <thinking> を含む推論過程を出力するモデルを構築しています。ここで公開しているのは 推論ありモデル です。
学習データ
日本語の医療画像テキスト対データは公開規模が限られているため、本モデルでは既存の英語医療データをもとに、日本語の大規模学習データを構築しました。 全学習データはMIL-UT/Japanese-Medical-VQA-12mにて公開しています。
最終的に、Stage1, 2 用のキャプションデータとして 12,125,556 件、Stage3 用の VQA データとして 12,125,203 件を用いています。
モデル構成
本モデルは LLaVA ベースのエンコーダ・デコーダ型 VLM です。
| Model components | Model | Parameters |
|---|---|---|
| Image encoder | google/siglip2-so400m-patch16-512 | 428,772,800 |
| Projectpr | 2層 MLP | 64,240,640 |
| LLM | SIP-med-LLM/SIP-jmed-llm-3-13b-OP-4k-base | 13,707,924,480 |
| 合計 | 14,200,937,920 |
学習は 3段階で行っています。
| Stage | 学習対象 | 訓練データ |
|---|---|---|
| Stage1 | プロジェクター層 | Image + Caption |
| Stage2 | プロジェクター層, テキストデコーダ | Image + Enriched caption |
| Stage3 | プロジェクター層, テキストデコーダ | Image + VQA |
学習には Megatron-LM を用いました。
評価結果
本モデルは、以下の 2 種類の評価で有効性を確認しています。
- CT 画像に対する日本語 VQA
- 胸部 X 線画像に対する日本語読影レポート生成
LLM as a Judgeの評価については医療専門家のフィードバックを受けて、言語処理学会で発表したプロンプトを改変しております。
CT 画像に対する日本語 VQA
| Model | Size | ROUGE-L |
|---|---|---|
| Gemma | 27B | 15.99 |
| Phi4 | 6B | 36.31 |
| InternVL | 38B | 24.88 |
| vila_jp | 14B | 40.48 |
| Sarashina | 14B | 17.28 |
| Asagi | 14B | 29.13 |
| Llava med | 8B | 0.90 |
| 推論あり | 14B | 46.47 |
| 推論なし | 14B | 27.36 |
胸部 X 線画像に対する日本語読影レポート生成
| Model | ROUGE-L | LLM as a Judge |
|---|---|---|
| GPT 5 | 16.11 | 4.05 |
| GPT 4.1 | 13.95 | 3.18 |
| Gemma | 15.50 | 2.12 |
| Phi4 | 16.10 | 2.76 |
| InternVL | 16.77 | 2.80 |
| vila_jp | 16.57 | 2.82 |
| Sarashina | 10.49 | 2.17 |
| Asagi | 16.18 | 2.04 |
| Llava med | 0.05 | 1.00 |
| 推論あり | 15.89 | 3.40 |
| 推論なし | 11.31 | 1.72 |
| 推論あり(SFT) | 30.04 | 3.50 |
| 推論なし(SFT) | 30.16 | 3.14 |
使用方法
Requirements
transformers==4.45.1
accelerate==0.34.2
torch==2.4.0
torchvision==0.19.0
How to use
import requests
import torch
from PIL import Image
from transformers import AutoModel, AutoProcessor, GenerationConfig
model_path = "MIL-UT/Med-Asagi-14B-reasoning"
processor = AutoProcessor.from_pretrained(model_path)
model = AutoModel.from_pretrained(
model_path, trust_remote_code=True,
torch_dtype=torch.bfloat16,
device_map="auto"
)
generation_config = GenerationConfig(
do_sample=True,
num_beams=5,
max_new_tokens=512
)
prompt = ("以下は、タスクを説明する指示です。要求を適切に満たす応答を書きなさい。\n\n"
"### 指示:\n<image>\nこの画像を見て、異常所見を述べてください。\n\n### 応答:\n")
# sample image
sample_image_url = "https://www.ringe.jp/files/civic/20190906/img/02-1.jpg"
image = Image.open(requests.get(sample_image_url, stream=True).raw)
inputs = processor(
text=prompt, images=image, return_tensors="pt"
)
inputs_text = processor.tokenizer(prompt, return_tensors="pt")
inputs['input_ids'] = inputs_text['input_ids']
inputs['attention_mask'] = inputs_text['attention_mask']
for k, v in inputs.items():
if v.dtype == torch.float32:
inputs[k] = v.to(model.dtype)
inputs = {k: inputs[k].to(model.device) for k in inputs if k != "token_type_ids"}
generate_ids = model.generate(
**inputs,
generation_config=generation_config
)
generated_text = processor.batch_decode(
generate_ids, skip_special_tokens=True, clean_up_tokenization_spaces=False
)[0]
# do not print the prompt
if "<image>" in prompt:
prompt = prompt.replace("<image>", " ")
generated_text = generated_text.replace(prompt, "")
print(f"Generated text: {generated_text}")
出力例:
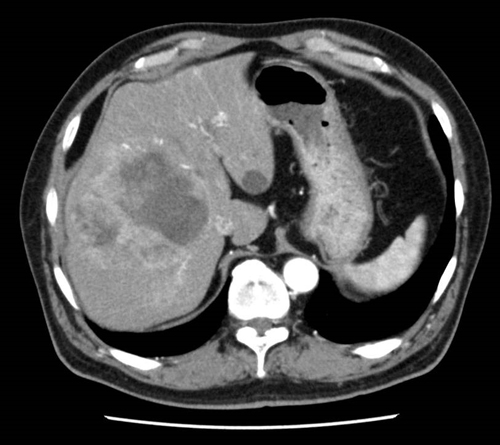
<description>
- 画像は腹部の横断CTスキャンです。
- 肝臓は画像の左側に位置し、右葉に大きく不規則な形状の腫瘤が見られます。
- その腫瘤は密度が不均一で、低密度領域と高密度領域が混在しています。
- 腫瘤の周囲の肝実質は比較的均一な密度を示しています。
- 胃は画像の右側にあり、部分的に内容物が入っています。
- 脾臓は胃の隣に位置し、均一な密度を示しています。
- 脊柱は画像の下部中央にあり、椎体と脊髄管が確認できます。
- 大動脈と下大静脈は脊柱の前方に円形の構造として見えます。
- 肋骨は画像の周辺部に曲線状の高密度構造として描かれています。
- 腹腔内に自由液やガスは認められません。
</description>
<thinking>
まず、画像全体を確認すると、肝臓の右葉に大きく不規則な形状の腫瘤が存在することが分かります。この腫瘤は密度が均一でなく、低密度領域と高密度領域が混在しているため、組織構成が不均一であることが示唆されます。腫瘤の周囲の肝実質は比較的均一な密度を保っており、腫瘤自体が肝臓内部に局在していることが確認できます。
他の臓器(胃、脾臓、脊柱、大動脈・下大静脈、肋骨)はそれぞれ正常な形態と密度で描写されており、特に異常所見は見られません。また、腹腔内に自由液やガスがないことから、急性の腹膜炎や穿孔などの合併症は起きていないと考えられます。
以上の観察結果から、画像上で最も顕著な異常は肝臓右葉に位置する大きく不規則で密度が不均一な腫瘤であると結論付けられます。
</thinking>
答え: 肝臓右葉にある大きく不規則で密度が不均一な腫瘤が画像上の異常所見です。
使用上の注意
- 本モデルは研究開発段階のプロトタイプであり、実臨床における安全性・有効性の検証は十分に行われていません。
- 開発者は、本プログラムに関し、その正確性、完全性、最新性、および品質など、いかなる保証も行わず、利用者が本プログラムを利用したこと、利用できなかったことにより生じた一切の損害について責任を負いません。
- 医療行為(診断、治療方針の決定、健康への助言など)に直接適用することは推奨されません。あくまで医療専門家による適切な判断の補助となる情報提供ツールとしての利用可能性を探る研究段階にあります。
- 公開しているモデルを活用して「具体的な製品」を開発される場合、その製品が医療機器プログラムとして薬機法の規制対象となる可能性があることにご留意ください。
- プログラム医療機器の該当性に関する相談窓口:
- 独立行政法人医薬品医療機器総合機構(PMDA; Pharmaceuticals and Medical Devices Agency)
ライセンス
cc-by-sa-4.0
引用
本モデルを利用した場合は、以下の論文を引用ください。
@inproceedings{ando2026japanese_medical_vlm,
title={医療用大規模日本語視覚言語モデルの構築},
author={安道 健一郎 and 黒瀬 優介 and 菊地 智博 and 牧元 久樹 and 小寺 聡 and 小林 和馬 and 合田 和生 and 村尾 晃平 and 吉田 浩 and 田村 孝之 and 合田 憲人 and 喜連川 優 and 原田 達也},
booktitle={言語処理学会第32回年次大会},
year={2026}
}
メンテナンス情報
問い合わせ先: ando [at] mi.t.u-tokyo.ac.jp までご連絡ください。
- Downloads last month
- 98